2026年3月23日 抗インフルエンザ剤感受性低下株調査の結果
2025-2026年シーズンの日本におけるインフルエンザ流行株と抗インフルエンザ薬感受性低下株調査の概要(2026年3月23日時点)
2025年10月から2026年3月23日までの期間にわたり、日本各地でのインフルエンザ流行状況および薬剤耐性変異を持つインフルエンザウイルスの発生状況を調査しました。本調査では、バロキサビルに対する感受性が低下するPA遺伝子の変異、およびオセルタミビルを含むノイラミニダーゼ阻害剤に対する感受性が低下するNA遺伝子の変異を検出しました。
全国8道府県の外来医療機関が本研究に協力しました。発熱、咳、喉の痛み、だるさなど、インフルエンザが疑われる症状(インフルエンザ様疾患、ILI)がある患者のうち、迅速診断テスト(RDT)でインフルエンザA型またはB型陽性と判定された方から、上気道検体を採取し、これを初診時のサンプルとしました。また、バロキサビルを投与された患者には、3~7日後に再診をお願いし、その際に再診時の上気道検体を採取しました。これらの検体はすべて新潟大学に送付され、リアルタイムPCR(RT-PCR)法を用いてインフルエンザウイルスの検出、型/亜型の判定、PA/I38T変異の検出(A(H1N1)pdm09とA(H3N2)に対し)、NA/H275Y変異の検出(A(H1N1)pdm09に対し)を行いました。次世代シーケンシング(NGS)法とサンガー法を用いて、PA変異及びNA変異を確認しました。
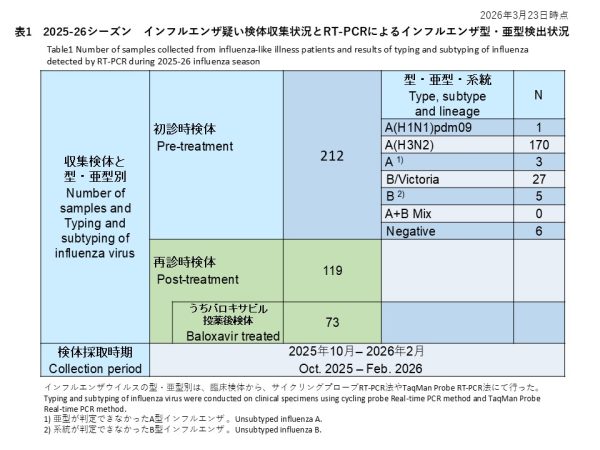
【初診時検体】
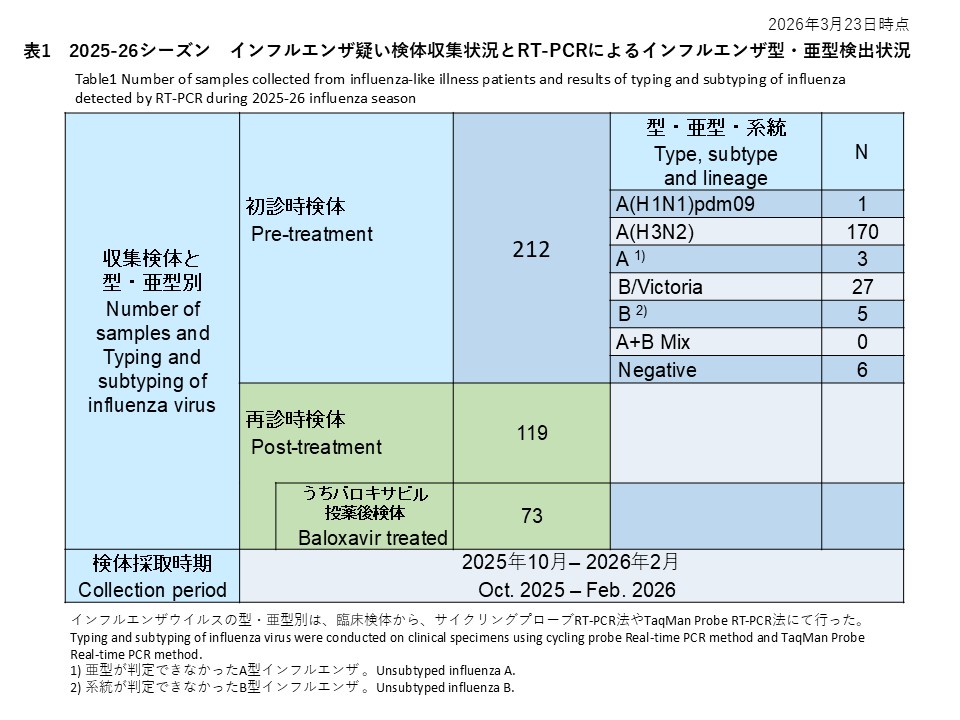
初診時に採取された212件の検体の内訳は、インフルエンザウイルスA(H1N1)pdm09が1件(0.5%)、インフルエンザウイルスA(H3N2)が170件(80.2%)、亜型判定不能のA型インフルエンザウイルスは3件(1.4%)、インフルエンザウイルスB/Victoriaが27件(12.7%)、系統が判定できなかったB型インフルエンザが5件(2.4%)でした。また、A型およびB型の混合感染は0件(0.0%)、RT-PCR陰性の検体は6件(2.8%)でした(表1)。
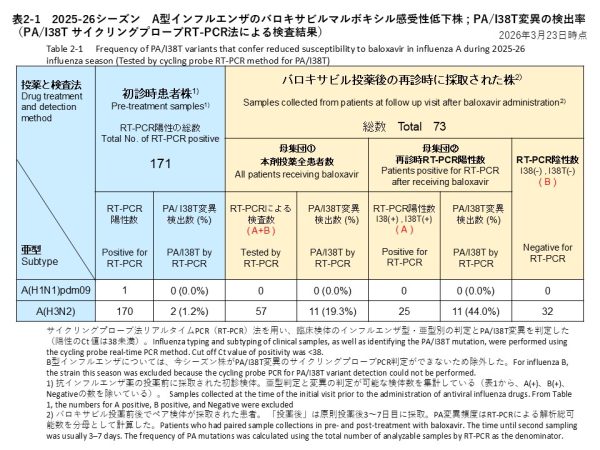
治療前に採取されたインフルエンザA型の検体について、サイクリングプローブRT-PCR法によりPA/I38T変異の検出を試みた結果、1件のA(H1N1)pdm09は検出なし(検出率:0.0%)、170件のA(H3N2)のうちPA/I38T変異陽性の検体が2検体確認されました(検出率:1.2%)(表2-1)。
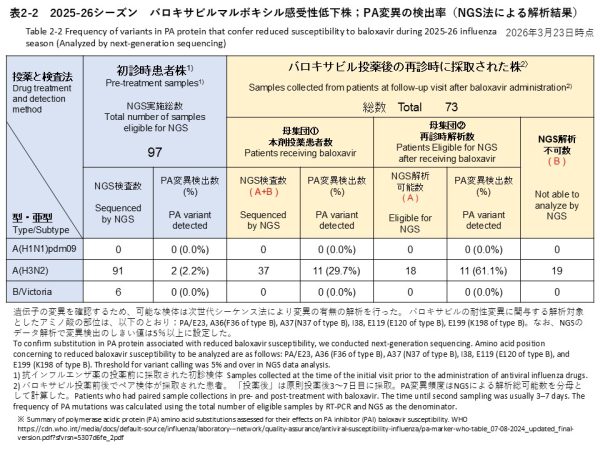
次世代シークエンス解析は、初診時検体212件のうちA(H3N2) 91件、B/Victoria 6件を対象に実施しました。その結果、バロキサビル耐性に関連するPA/I38T変異をA(H3N2)で 2件検出しました(検出率:2.2%)(表2-2)。これら2検体のバリアントコール解析では、PA/I38T変異の割合が98%以上であり、野生型はほとんど検出されず、PA/I38T変異ウイルスがほぼ全てを占める状態でした。1例は初診時検体のみで、臨床経過の詳細は確認できていません。もう1例は、治療はバロキサビルで行われました。有熱時間は4.8時間でした。再診検体も採取されましたが、ウイルス量が少なく解析できませんでした。
また、初診時のA(H3N2)検体1件で、NGSバリアントコール(変異検出閾値5%)によりPA/E23Vが5.7%検出されました。E23Vは耐性関連変異リスト(例:E23G/K/R)に含まれず文献報告も確認できないため、参考所見として記載します(表2‐2には感受性株として計上)。
サンガー法によるPA遺伝子変異の解析は、現時点では未実施です。
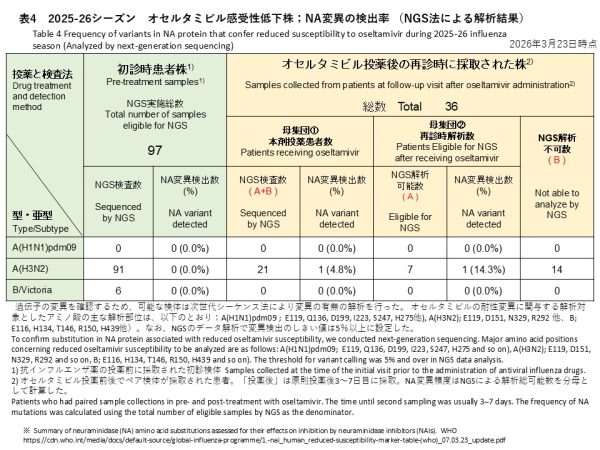
A(H3N2) 91件、B/Victoria 6件から、オセルタミビルに対する感受性低下に関連するNA遺伝子変異は、次世代シークエンス法で検出されませんでした(表4)。
【再診時検体】
再診時検体は119名から採取され、73件がバロキサビル投与後、36件がオセルタミビル投与後の検体でした(表2-2、表4)。
これらの検体に対して、サイクリングプローブRT-PCR法を用いてPA/I38T変異の有無を調べた結果、A(H3N2) 57検体中11検体でPA/I38T変異が検出されました(検出率:19.3%)。このうち1検体は、PA/I38T変異のあるウイルスのみが検出され、他10検体はバロキサビル感受性株と耐性変異株が混在していると考えられました。混在例のうち1例は、再診の1日後にもう一回検体が採取されており、その検体からはPA/I38T変異株のみ検出されました。
また、再診時にRT-PCRでインフルエンザA(H3N2)が陽性であった25検体を分母とした場合、PA/I38T変異は11検体で検出され、検出割合は44.0%(11/25)でした(表2-1)。
バロキサビル投与後の37検体(全てA(H3N2))のNGS解析を実施しました。18件でデータ解析が可能で、PA遺伝子の変異は11件で確認されました。PA変異の検出率は解析数37件を分母とすると29.7%(11/37)、解析が成功した18件を分母とすると61.1%(11/18)でした。確認された変異の内訳は、PA/I38Tが7件(バリアントコール:7.4~54.7%)、PA/I38Mが3件(バリアントコール:6.8~35.4%)、PA/I38TとPA/I38Mが同時に検出された検体が1件(PA/I38T:10.4%、PA/I38M:14.4%)でした。これらの11例のPA変異を有するA(H3N2)症例について、バロキサビル投与後の有熱時間の中央値は、33時間でした(範囲:0-128時間)。
オセルタミビル投与後の再診時に採取された21件(すべてA(H3N2))に対しNGS解析を実施し、うち7件でデータ解析が可能でした(表4)。そのうち1件からNA遺伝子の変異が検出され、検出率は全体(21件)で4.8%、解析可能検体(7件)では14.3%でした。検出された変異は、NA/N295S変異(バリアントコール:39.6%)でした。
Overview of Influenza Circulating Strains and Antiviral Drug-Resistant Strains in Japan During the 2025-2026 Season (As of March 23, 2026)
Between October 2025 and March 23, 2026, we conducted a study in Japan to monitor circulating influenza strains and the emergence of antiviral resistance. The study focused on detecting substitutions in the PA gene associated with reduced susceptibility to baloxavir and substitutions in the NA gene associated with reduced susceptibility to neuraminidase inhibitors, including oseltamivir.
Participating Medical Institutions and Sample Collection
Outpatient medical institutions in eight prefectures participated in this study. Upper respiratory tract samples were collected as initial samples from patients who visited these institutions with suspected influenza symptoms (influenza-like illness, ILI), such as fever, cough, sore throat, and fatigue. These patients were confirmed positive for influenza A or B using rapid diagnostic tests (RDTs). For patients treated with baloxavir, upper respiratory tract samples were also collected during follow-up visits 3–7 days after treatment. All clinical specimens were sent to Niigata University, where real-time RT-PCR was performed for influenza virus detection, type/subtype determination, detection of the PA/I38T substitution (for A(H1N1)pdm09 and A(H3N2)), and detection of the NA/H275Y substitution (for A(H1N1)pdm09). Next-generation sequencing (NGS) and Sanger sequencing were used to confirm PA and NA substitutions.
Baseline (pre-treatment) specimens
Among 212 baseline specimens, influenza A(H1N1)pdm09 was detected in 1 specimen (0.5%), influenza A(H3N2) in 170 specimens (80.2%), unsubtyped influenza A in 3 specimens (1.4%), influenza B/Victoria in 27 specimens (12.7%), and influenza B with undetermined lineage in 5 specimens (2.4%). No mixed A and B infections were identified (0.0%), and 6 specimens (2.8%) were RT-PCR negative (Table 1).
For baseline pre-treatment influenza A specimens, we screened for the PA/I38T substitution using the cycling-probe RT-PCR method. PA/I38T-positive specimens were identified in 2 of 170 A(H3N2) specimens (detection rate: 1.2%) and no PA/I38T was identified in one A(H1N1)pdm09 positive specimen. (Table 2-1).
NGS analysis was performed for 91 A(H3N2) and 6 B/Victoria specimens among the 212 baseline specimens collected at the initial visit. As a result, the PA/I38T substitution associated with reduced susceptibility to baloxavir was detected in 2 A(H3N2) specimens (detection rate: 2.2%) (Table 2-2). Variant-calling analysis of these two specimens showed that the PA/I38T variant frequency was ≥98%, indicating that wild-type virus was barely detectable and that the PA/I38T variant population accounted for almost the entire viral population in the specimens. One case had only a baseline specimen collected, and detailed clinical course information could not be confirmed. In the other case, baloxavir was used for treatment, and the fever duration was 4.8 hours. A follow-up specimen was collected from this case, but the viral load was low and sequencing analysis was not successful.
In addition, in one baseline A(H3N2) specimen, PA/E23V was detected at 5.7% by NGS variant calling (variant detection threshold: 5%). Because E23V is not included in the list of baloxavir resistance-associated substitutions by WHO (e.g., E23G/K/R) and no published reports have been identified, this finding is described as a reference (this sample is counted as a susceptible virus in Table 2-2).
Sanger sequencing for PA gene substitutions has not been performed to date.
No NA gene substitutions associated with reduced susceptibility to oseltamivir were detected by NGS in the 91 A(H3N2) and 6 B/Victoria baseline specimens (Table 4).
Follow-up (post-treatment) specimens
Follow-up (post-treatment) specimens were collected from 119 patients. Among them, 73 patients provided upper respiratory tract specimens 3–7 days after the start of baloxavir treatment and 36 patients provided the specimens after the Oseltamivir treatment. (Table 2-2. Table 4).
Using the cycling-probe RT-PCR method, PA/I38T was detected in 11 of the 57 A(H3N2) follow-up specimens (detection rate: 19.3%). In one specimen, only the PA/I38T variant virus was detected, whereas in the remaining 10 specimens, baloxavir-susceptible virus and resistance-associated variants were considered to coexist. Among the mixed cases, one patient had an additional specimen collected one day after the follow-up visit, from which only the PA/I38T variant virus was detected. When analysis was restricted to the 25 follow-up specimens that were RT-PCR positive for influenza A(H3N2), PA/I38T was detected in 11 specimens, corresponding to a detection proportion of 44.0% (11/25) (Table 2-1).
NGS analysis was conducted for the 37 post-baloxavir specimens (all A(H3N2)). Sequencing analysis was successful in 18 specimens, and PA gene substitutions were identified in 11 of these specimens. The detection rate of PA substitutions was 29.7% (11/37) when calculated using all 37 specimens as the denominator, and 61.1% (11/18) when calculated using the 18 specimens with successful NGS analysis as the denominator. The detected substitutions consisted of PA/I38T in 7 specimens (variant call frequencies: 7.4–54.7%), PA/I38M in 3 specimens (variant call frequencies: 6.8–35.4%), and co-detection of both PA/I38T and PA/I38M in 1 specimen (PA/I38T: 10.4%; PA/I38M: 14.4%). Among the 11 A(H3N2) cases with PA substitutions detected after baloxavir treatment, the median fever duration after baloxavir administration was 33 hours (range: 0–128 hours).
NGS analysis was performed for 21 A(H3N2) specimens collected at follow-up after oseltamivir treatment. In the 7 specimens for which analysis was successful, one NA gene substitution associated with reduced susceptibility to oseltamivir was detected by NGS (Table 4). The detection rate of NA substitutions was 4.8% (1/21) when calculated using all 21 specimens as the denominator, and 14.3% (1/7) when calculated using the 7 specimens with successful NGS analysis as the denominator. Detected substitution was NA/N295S (variant frequency: 39.6%).